Evolutionäre Neuentwicklungen können auch in „neutraler“ DNA entstehen
Archivmeldung vom 02.11.2011
Bitte beachten Sie, dass die Meldung den Stand der Dinge zum Zeitpunkt ihrer Veröffentlichung am 02.11.2011 wiedergibt. Eventuelle in der Zwischenzeit veränderte Sachverhalte bleiben daher unberücksichtigt.
Freigeschaltet durch Thorsten Schmitt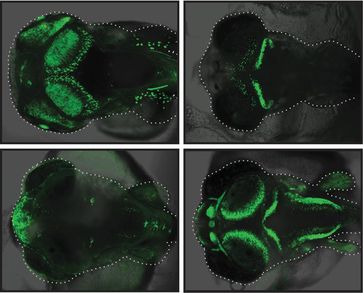
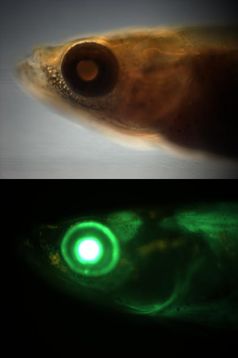
Der größte Teil des menschlichen Erbgutes besteht aus DNA ohne offensichtliche Funktion, der sogenannten „neutralen“ oder „Junk-DNA“. Die Wissenschaftler Dr. Laurence Ettwiller und Michael Eichenlaub vom Centre for Organismal Studies der Universität Heidelberg konnten nun diese „Dunkle Materie“ des Erbgutes als Quelle für evolutionäre Neuentwicklungen identifizieren. Ihre Studie zeigt, dass schon wenige Veränderungen in funktionell inaktiver „Junk-DNA“ ausreichen, um wichtige Steuerelemente der Genregulation, die Enhancer, neu entstehen zu lassen. Die Forschungsergebnisse werden am 1. November 2011 in „PLoS Biology“ veröffentlicht.
Genetische Unterschiede zwischen Menschen werden weniger von Differenzen in den 1,5 Prozent des Erbguts bestimmt, die für Genprodukte kodieren. Vielmehr gehen Experten heute davon aus, dass zur Vielfalt innerhalb der Spezies Homo sapiens vor allem Veränderungen in denjenigen Abschnitten der DNA beitragen, die die Genregulation, das heißt die Bildung von Genprodukten wie Proteinen, beeinflussen. Ein wesentliches Steuerelement der Genregulation sind „Verstärker“, die Enhancer. Veränderungen in Enhancern sind einerseits Ursache zahlreicher Krankheiten und Fehlbildungen. Andererseits bergen sie das Innovationspotential für evolutionäre Neuentwicklungen.
Michael Eichenlaub und Laurence Ettwiller haben nun gezeigt, dass solche Innovationen durch die „de novo“-Bildung von neuen Enhancern entstehen können. Sie konnten belegen, dass nur geringe Veränderungen in der DNA-Sequenz ausreichen, um neue regulatorische Elemente aus nicht-regulatorischer „Junk-DNA“ entstehen zu lassen. Diese Beobachtung steht im Kontrast zur allgemeinen Annahme unter Evolutionsforschern, dass evolutionäre Neuentwicklung überwiegend auf der Modifikation prä-existenter funktioneller Elemente des Genoms basiert. Diese Sichtweise hat dazu beigetragen, dass Forscher ihr Augenmerk bisher fast ausschließlich auf Veränderungen funktionell aktiver Genomelemente gerichtet haben. Veränderungen innerhalb „neutraler“ oder „Junk-DNA“ – den etwa 97 Prozent der Erbinformation, die auch als die „Dunkle Materie“ des Genoms bezeichnet werden – wurden dagegen vernachlässigt. „Unsere Arbeit wirft ein Licht auf diese vernachlässigten Abschnitte des Genoms, die ein Spielfeld zur Herstellung neuer Enhancer sein dürften“, sagt Studienleiterin Laurence Ettwiller.
Die Heidelberger Wissenschaftler verwendeten für den Beweis dieser neuen Enhancer einen experimentellen Ansatz in dem japanischen Süßwasserfisch Medaka. Sie testeten verwandte Sequenzen von verschiedenen Spezies auf Enhancer-Aktivität und konnten in mehreren Fällen die Existenz neu entstandener Enhancer aus nicht-funktioneller „Junk-DNA“ zeigen. Auch wenn die Studie in Fischen durchgeführt wurde, ist davon auszugehen, dass beim Menschen identische Mechanismen zur evolutionären Neuentwicklung existieren, wie Laurence Ettwiller erläutert.
„Die Studie beweist, dass die winzigen Veränderungen im Erbgut, die sich von Generation zu Generation ansammeln, ausreichen, um neue Funktionen ,aus dem Nichts‘ entstehen zu lassen“, erläutert Michael Eichenlaub. „Unsere Methode könnte dabei helfen, Veränderungen zu verstehen, die zur Entwicklung unserer Spezies geführt haben“, so Dr. Ettwiller, „und die funktionelle Bedeutung der 1,23 Prozent der Erbinformation zu entschlüsseln, in denen sich das menschliche Genom von dem des Schimpansen unterscheidet.“
Weitere Informationen können im Internet unter www.cos.uni-heidelberg.de/forschung/ettwiller/index.html abgerufen werden.
Quelle: Ruprecht-Karls-Universität Heidelberg (idw)